Dr. Antonio Lagares
CARACTERIZACIÓN GENÓMICA Y FUNCIONAL DE PLÁSMIDOS AISLADOS DEL AMBIENTE
Antonio Lagares, Mariano Pistorio, María Florencia Del Papa
Empleamos una aproximación genómica (basada en secuenciamiento masivo y bioinformática) y funcional para la exploración y recuperación de actividades biológicas plasmídicas de microorganismos a partir de comunidades microbianas sometidas a presiones de selección específicas vinculadas a la presencia de compuestos recalcitrantes. Las mismas podrían ser aplicables a procesos de bioremediación necesarios por el uso de determinadas prácticas agrícolas.

Así también, el conocimiento de los plásmidos de dicho ambiente nos permitirá avanzar en el estudio de funciones directamente asociadas a los mismos, como la replicación, estabilización, partición y movilización. El conocimiento de la información contenida en estos plásmidos podrá facilitar la predicción de la secuencia de proteínas con potencial uso en aplicaciones biotecnológicas o terapéuticas, y enzimas con potencial aplicación en el catabolismo de compuestos recalcitrantes xenobióticos, como pesticidas y herbicidas, o de interés tecnológico/industrial.
CARACTERIZACIÓN MOLECULAR Y FENOTÍPICA DEL MICROBIOMA BACTERIANO CULTIVABLE ASOCIADO A SEMILLAS Y PLANTAS DE ALFALFA
José Luis López, Antonio Lagares
Las evidencias actuales muestran a las plantas como organismos naturalmente muy colonizados, tanto en su exterior (rizósferas y filósferas) como en su interior, por una diversidad muy grande de microorganismos. Si bien la mayoría de ellos actúan como comensales sin ningún efecto conocido sobre las plantas que colonizan, múltiples bacterias y hongos establecen con sus hospedantes relaciones ya sea mutualistas o de carácter patogénico.
En dicho contexto, el resultado del comportamiento del sistema en un ambiente particular (fitness) resulta de la interacción del conjunto de los genes del huésped y los de todo su microbioma asociado (i.e. el hologenoma). De este modo, la unidad de selección a lo largo del tiempo está constituida por la propia planta y por todo su microbioma (i.e. el holobionte).
Un aspecto particularmente importante de las asociaciones entre plantas y microorganismos es el relacionado con la heredabilidad y la dinámica de los microbiomas. Los microorganismos que colonizan semillas y raíces han recibido la mayor atención, con información que apoya la existencia de mecanismos de transmisión que incluyen la vía sistémica (in planta), horizontal (entre plantas) y vertical (a lo largo de generaciones).
Bajo este modelo, la carga microbiana endofítica de semillas sanas parece ser al menos parcialmente heredada a través de generaciones, representando un inóculo inicial importante de las plántulas nacientes que luego compite con miembros de la comunidad del suelo que arriban más tardíamente.
Todas estas consideraciones posicionan al estudio de los microbiomas vegetales como un objetivo central para comprender las respuestas y evolución de las plantas en su ambiente natural, así como para hacer un uso práctico racional de las actividades benéficas presentes.
Resultados recientes de nuestro grupo orientados a caracterizar la población endofítica de semillas de alfalfa esterilizadas en superficie, revelaron la presencia de bacterias de más de 40 géneros diferentes pertenecientes a 4 phylas distintos: Proteobacteria, Actinobacteria, Firmicutes y Bacteroidetes. La posición taxonómica de dichos aislamientos fue inferida por secuenciamiento parcial de regiones del rDNA 16S y tecnología MALDI-TOF Biotyper™ Brucker.
Entre los aislamientos presentes sin excepción en al menos 3 de las 6 variedades de alfalfa analizadas, se encontraron miembros de los géneros Arseniciccocus, Arthrobacter, Bacillus, Kocuria, Microbacterium, Microccocus y Paenibacillus. Con menor ubicuidad, otro género frecuente fue Pantoea sp., presente en números elevados comparados con el resto de los endófitos de semilla.
La colección de más de 240 aislamientos endofíticos de alfalfa se encuentra preservada a -80°C como parte del cepario del grupo en el IBBM. En clones representantes de los diferentes géneros que colonizan alfalfa, se investigan características fenotípicas asociadas a la promoción del crecimiento vegetal y al biocontrol, además de definir sistemas modelo para el estudio de los determinantes genéticos requeridos para la colonización endofítica de raíces y parte aérea de las plantas hospedadoras.
BÚSQUEDA, IDENTIFICACIÓN Y CARACTERIZACIÓN FUNCIONAL -A ESCALA GENÓMICA- DE DETERMINANTES GENÉTICOS DE RIZOBIOS REQUERIDOS PARA LA COLONIZACIÓN DE LA RIZÓSFERA
María Eugenia Salas, Mauricio Javier Lozano, Antonio Lagares
Los rizobios son α- y β-proteobacterias habitantes del suelo que poseen la capacidad de asociarse en simbiosis con raíces de plantas leguminosas...
En ese proceso, el número de nódulos finales está cuidadosamente regulado para evitar infecciones innecesarias que son energéticamente costosas para la planta...
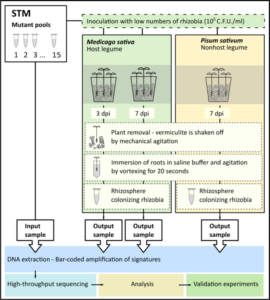
A pesar del detallado conocimiento actual del proceso de infección y desarrollo de nódulos...
El avance espectacular de los últimos años en la disección del proceso simbiótico...
El proyecto enfoca la identificación de genes simbióticos asociados al abordaje inicial...

ESTUDIOS FUNCIONALES Y ECOLÓGICOS DE MICROORGANISMOS DEL SUELO PARA UNA PRODUCCIÓN AGRÍCOLA SUSTENTABLE
Walter Draghi, Antonio Lagares
La sustentabilidad de los sistemas agrícolas es clave para mantener la productividad de los recursos naturales.
El uso de microorganismos rizosféricos mejora la resistencia de los cultivos frente a condiciones ambientales adversas, promoviendo un crecimiento vegetal saludable.

Se analizan dos ejes principales:
1. Búsqueda de cepas inoculantes más persistentes y eficientes para simbiosis en suelos ácidos.
Se estudian las bases bioquímicas y genéticas de la adaptación a la acidez en Sinorhizobium meliloti, usando técnicas ómicas de expresión global.
Además, se generan fenotipos resistentes (ATR) con mayor capacidad de infección bajo estrés ácido.

2. Estudio de la ecología poblacional de Burkholderia spp. en suelos agrícolas argentinos.
MICROBIOLOGÍA AMBIENTAL Y EVOLUCIÓN DE BACTERIAS DEL SUELO
Mauricio Lozano, Walter Draghi, Antonio Lagares
En el laboratorio investigamos cómo las bacterias del suelo se adaptan a distintos nichos ecológicos y cómo factores como la acidez, la disponibilidad de nutrientes y la presencia de contaminantes moldean su evolución y estructura poblacional.
Nos enfocamos en comunidades rizosféricas y bacterias libres del suelo, integrando herramientas de genómica comparativa, filogenómica y bioinformática avanzada.
A través de estudios de evolución experimental, analizamos la capacidad de cepas nativas para adquirir nuevas funciones adaptativas frente a presiones ambientales, con especial interés en la transferencia horizontal de genes y la dinámica de plásmidos.

Estos estudios contribuyen a comprender los mecanismos de adaptación bacteriana y su potencial aplicación en biotecnología, restauración de suelos degradados y desarrollo de biofertilizantes más eficientes.
GENÓMICA FUNCIONAL DE BACTERIAS DE INTERÉS AGRÍCOLA Y BIOTECNOLÓGICO
Mauricio Lozano, Antonio Lagares, Gonzalo Torres Tejerizo
Este proyecto se centra en la secuenciación, ensamblado y anotación funcional de genomas bacterianos aislados de suelos agrícolas de distintas regiones del país.
Buscamos identificar genes asociados con tolerancia al estrés, producción de metabolitos secundarios y mecanismos de interacción planta–microorganismo.
La información genómica obtenida es analizada mediante técnicas de minería de datos y comparación con bases de datos internacionales, lo que permite descubrir nuevos genes de interés biotecnológico y aportar al desarrollo de inoculantes bacterianos de nueva generación.
Este enfoque integrador entre genómica funcional y biología de sistemas proporciona una base sólida para el desarrollo de productos agrícolas más sostenibles y eficientes.

ESTUDIO DE LA INTERACCIÓN BACTERIA–HOSPEDADOR EN SISTEMAS SIMBIÓTICOS Y PATOGÉNICOS
María Carla Martini, Antonio Lagares, Gonzalo Torres Tejerizo
En nuestro grupo abordamos el estudio de las interacciones moleculares y celulares entre bacterias y hospedadores, tanto en relaciones benéficas como patogénicas.
Buscamos entender cómo las bacterias modulan su expresión génica frente a señales del hospedador y cómo estos mecanismos determinan el éxito o fracaso de la colonización.
Utilizamos aproximaciones genómicas, transcriptómicas y proteómicas para identificar determinantes moleculares en la simbiosis o infección.
Estas herramientas permiten analizar globalmente la respuesta bacteriana, identificar reguladores clave y comprender cómo ajustan su metabolismo y fisiología para adaptarse al entorno del hospedador.

Este conocimiento es clave para desarrollar estrategias biotecnológicas que mejoren inoculantes agrícolas o terapias antimicrobianas sostenibles.
Dr. Mariano Pistorio
LOS PLÁSMIDOS Y SU ROL EN LA TRANSFERENCIA HORIZONTAL DE GENES
Lucas Castellani, Ileana Salto, Gonzalo Torres Tejerizo, Mariano Pistorio
Los plásmidos son elementos más pequeños que los cromosomas bacterianos y contienen en su estructura molecular genes que generalmente no se encuentran en el cromosoma. Si bien estos elementos contribuyen a la diversidad y plasticidad genética de los microorganismos, no son, en principio, esenciales para la vida microbiana, y por lo tanto, constituyen un recurso genético distinto, dinámico y adicional a los genes cromosomales. La importancia de los plásmidos se debe a su papel preponderante en la transferencia horizontal de genes dentro de las poblaciones bacterianas y como herramientas para la manipulación genética.
Los plásmidos permiten a las poblaciones bacterianas “muestrear” el pool de elementos genéticos móviles (moviloma) buscando así rasgos adaptativos que puedan ser ventajosos para la supervivencia bajo presiones selectivas locales, como resistencia a antibióticos, metales y contaminantes orgánicos del ambiente o la capacidad de utilizar fuentes de carbono alternativas.
En el laboratorio estamos interesados en el aislamiento, secuenciamiento y caracterización funcional de los recursos genéticos asociados a plásmidos presentes en la comunidad bacteriana relacionada a ambientes tan distintos como los ambientes agrícola y hospitalario.
El análisis detallado de los plásmidos representa una poderosa herramienta para avanzar en el conocimiento de sus secuencias génicas; en particular, nos permitirá el estudio de funciones adaptativas y/o de relevancia biotecnológica portadas en los mismos.
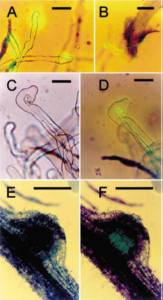
De esta manera se espera obtener nuevos datos sobre qué tipo de plásmidos se selecciona (grupo de incompatibilidad/tipo de origen de replicación) en cada uno de los ambientes y las relaciones que existen entre los distintos ambientes (interrelación/propagación de la información).
METAGENÓMICA APLICADA AL ESTUDIO DE MICROBIOMAS DE INTERÉS AGRÍCOLA. EFECTO DE LA BIOGEOGRAFÍA SOBRE EL MICROBIOMA DE LA VID
Mónica Oyuela Aguilar, Mariano Pistorio
En el marco de la agricultura sustentable, existe un creciente reconocimiento de la importancia económica y biológica de los microorganismos del suelo. La productividad de los suelos agrícolas depende en gran medida de distintos procesos llevados a cabo por las comunidades microbianas presentes en el suelo.
En la vitivinicultura, esta comunidad de microorganismos compleja y no del todo caracterizada juega un papel clave en las distintas etapas y en procesos de vinificación: desde ayudar a las plantas en el acceso de nutrientes del suelo y contribuir a la sanidad de la planta a través de protección contra patógenos, hasta el proceso de fermentación que transforma el mosto en vino con su complejo conjunto de aromas y sabores.
El conocimiento que se dispone actualmente sobre la estructura de comunidades microbianas está basado en aquellos microorganismos cuyo crecimiento se ha logrado en condiciones de laboratorio. El análisis metagenómico, consistente en la investigación de las comunidades microbianas a partir de ADN extraído directamente de muestras ambientales, permite encarar el estudio y la descripción de la complejidad microbiana del suelo independientemente del cultivo de la misma.
El plan propuesto fue concebido bajo la hipótesis de que, gracias a los recientes desarrollos en el estudio de la microbiología —principalmente debido a las nuevas técnicas de secuenciación—, se presenta una buena y única oportunidad para utilizar técnicas de laboratorio y bioinformáticas metagenómicas modernas con el fin de obtener una gran comprensión de los complejos procesos a través de los cuales los microbios se asocian con las vides y, en consecuencia, posteriormente afectan los vinos.
HERRAMIENTAS MICROBIOLÓGICAS, MOLECULARES Y ÓMICAS APLICADAS AL ESTUDIO DE LA INTERACCIÓN SIMBIÓTICA ENTRE RIZOBIOS Y LEGUMINOSAS
Juliet Nilsson, Gonzalo Torres Tejerizo, Mariano Pistorio
En el marco de una agricultura sustentable, la Fijación Biológica de Nitrógeno (FBN) realizada por bacterias en asociación simbiótica con leguminosas es un factor importante desde el punto de vista de la conservación de suelos y de la productividad agropecuaria, siendo la misma un evento crucial para asegurar la entrada de nitrógeno atmosférico a los suelos agrícolas.
La alfalfa es la leguminosa forrajera más cultivada para la alimentación animal y su asociación simbiótica con el rizobio eficiente, ya sea autóctono y/o inoculado, se ve afectada en suelos con pHs moderadamente bajos. Hace algunos años se aislaron, de suelos del centro de Argentina, un grupo de rizobios denominados Rhizobium favelukesii, tolerantes a la acidez y muy competitivos para la nodulación de alfalfa pero ineficientes en la FBN, presentando así características más parasíticas que simbióticas, que lo convierte en un potencial factor de riesgo al competir con el rizobio eficiente Ensifer (Sinorhizobium) meliloti.
La caracterización de los Rhizobium favelukesii contribuirá a entender aspectos básicos de la biología de los mismos, como la tolerancia a la acidez o mecanismos implicados en la fijación biológica de nitrógeno aún no descriptos.
Así, en un futuro cercano podremos evaluar la posibilidad de:
a) obtener en el entorno genético de los rizobios tipo Oregon una fijación biológica de nitrógeno eficiente, y/o
b) obtener variantes del simbiote eficiente E. meliloti que sean capaces de tolerar condiciones ácidas.
Ambas opciones tienen como finalidad aumentar la producción de alfalfa en los suelos agrícolas de Argentina.
CARACTERIZACIÓN GENÓMICA Y FUNCIONAL DE PLÁSMIDOS AISLADOS DEL AMBIENTE
Antonio Lagares, Mariano Pistorio, María Florencia Del Papa
Empleamos una aproximación genómica (basada en secuenciamiento masivo y bioinformática) y funcional para la exploración y recuperación de actividades biológicas plasmídicas de microorganismos a partir de comunidades microbianas sometidas a presiones de selección específicas vinculadas a la presencia de compuestos recalcitrantes. Las mismas podrían ser aplicables a procesos de bioremediación necesarios por el uso de determinadas prácticas agrícolas.

Así también, el conocimiento de los plásmidos de dicho ambiente nos permitirá avanzar en el estudio de funciones directamente asociadas a los mismos, como la replicación, estabilización, partición y movilización. El conocimiento de la información contenida en estos plásmidos podrá facilitar la predicción de la secuencia de proteínas con potencial uso en aplicaciones biotecnológicas o terapéuticas, y enzimas con potencial aplicación en el catabolismo de compuestos recalcitrantes xenobióticos, como pesticidas y herbicidas, o de interés tecnológico/industrial.
ANÁLISIS DE COMUNIDADES MICROBIANAS MEDIANTE SECUENCIACIÓN MASIVA
Mauricio Lozano, Mariano Pistorio, María Florencia Del Papa
Utilizando estrategias de metagenómica y metatranscriptómica, analizamos comunidades microbianas en diferentes ecosistemas del suelo, incluyendo agroecosistemas, ambientes naturales y sitios impactados por la actividad humana.
El objetivo es identificar los principales determinantes ecológicos que modelan la estructura y función microbiana.

Los datos generados son analizados mediante pipelines bioinformáticos que permiten la identificación taxonómica y funcional de los microorganismos, la predicción de rutas metabólicas y la detección de genes de resistencia o degradación de compuestos contaminantes.
Esta información es clave para entender cómo las comunidades microbianas responden a las prácticas agrícolas y cómo pueden ser aprovechadas para el diseño de estrategias sostenibles de manejo del suelo.
REGULACIÓN DE LA EXPRESIÓN GÉNICA EN RESPUESTA A CONDICIONES AMBIENTALES ADVERSAS
María Carla Martini, María Florencia Del Papa, Mariano Pistorio
Las bacterias deben responder rápidamente a los cambios ambientales para sobrevivir.
En este proyecto investigamos los sistemas reguladores de expresión génica que se activan frente a estrés por pH, salinidad, temperatura o nutrientes.

Se analizan sistemas de dos componentes y proteínas reguladoras transcripcionales y post-transcripcionales.
Los enfoques genómicos y fisiológicos permiten caracterizar redes regulatorias y entender cómo se coordinan respuestas adaptativas a nivel celular.
Los resultados amplían el conocimiento sobre la plasticidad metabólica bacteriana y su adaptación a condiciones fluctuantes del entorno natural.
Dra. María Florencia Del Papa
TRANSDUCCIÓN DE SEÑALES EN BACTERIAS
Carolina Vacca, Agustina Pérez, Juliana Heredia, Keila Belhart, María Florencia Del Papa
En el marco de una agricultura sustentable, la Fijación Biológica de Nitrógeno por rizobios en asociación simbiótica con leguminosas es un factor importante desde el punto de vista de la conservación de los suelos y la productividad agropecuaria. Debido a esto, el estudio de las asociaciones simbióticas rizobio-leguminosa ha sido muy activo, aumentando en forma considerable las posibilidades actuales de generar bacterias transgénicas con capacidades simbióticas superiores. Contrapuesto a los avances en este sentido, es poco lo que se conoce en relación a los determinantes genéticos involucrados en la tolerancia al estrés.
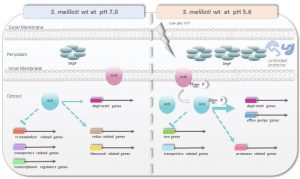
Desde el punto de vista práctico, el conocimiento de los mecanismos y procesos asociados con la tolerancia a un estrés será determinante para el diseño de estrategias que permitan mejorar las bacterias utilizadas para inocular un determinado suelo desfavorable.
En el grupo estamos concentrados en el estudio de señales externas que modulan la actividad biológica de sistemas de regulación transcripcional, y la caracterización funcional de estos sistemas y de los genes bajo su control, tomando la asociación Sinorhizobium meliloti-alfalfa como sistema modelo. Nuestros estudios involucran el uso de estrategias bioquímicas, genéticas y de biología molecular, incluyendo el uso de microscopía y análisis ómicos. Nos proponemos además concebir herramientas con potencial aplicación del conocimiento generado a la implementación y mejora de bioproductos con utilidad agro/tecnológica.
CARACTERIZACIÓN GENÓMICA Y FUNCIONAL DE PLÁSMIDOS AISLADOS DEL AMBIENTE
Antonio Lagares, Mariano Pistorio, María Florencia Del Papa
Empleamos una aproximación genómica (basada en secuenciamiento masivo y bioinformática) y funcional para la exploración y recuperación de actividades biológicas plasmídicas de microorganismos a partir de comunidades microbianas sometidas a presiones de selección específicas vinculadas a la presencia de compuestos recalcitrantes. Las mismas podrían ser aplicables a procesos de bioremediación necesarios por el uso de determinadas prácticas agrícolas.

Así también, el conocimiento de los plásmidos de dicho ambiente nos permitirá avanzar en el estudio de funciones directamente asociadas a los mismos, como la replicación, estabilización, partición y movilización. El conocimiento de la información contenida en estos plásmidos podrá facilitar la predicción de la secuencia de proteínas con potencial uso en aplicaciones biotecnológicas o terapéuticas, y enzimas con potencial aplicación en el catabolismo de compuestos recalcitrantes xenobióticos, como pesticidas y herbicidas, o de interés tecnológico/industrial.
CARACTERIZACIÓN SIMBIÓTICA Y MOLECULAR DE LOS RIZOBIOS NODULADORES DE Desmodium incanum EN ECOSISTEMAS DE ARGENTINA
María Antonieta Toniutti, María Florencia Del Papa
Nuestro grupo está interesado en caracterizar a nivel bioquímico y molecular los rizobios noduladores de Desmodium incanum, así como la asociación simbiótica entre ambos. Nos proponemos estudiar aspectos fisiológicos, bioquímicos y moleculares de las cepas aisladas de nódulos de Desmodium incanum recolectados en el campo y provenientes de ensayos de laboratorio.

Los estudios para avanzar en la estimación de la competitividad y de la capacidad de fijar nitrógeno de estos rizobios colaborarán en la tarea de seleccionar cepas más eficientes con potencial interés agronómico.
ANÁLISIS DE COMUNIDADES MICROBIANAS MEDIANTE SECUENCIACIÓN MASIVA
Mauricio Lozano, Mariano Pistorio, María Florencia Del Papa
Utilizando estrategias de metagenómica y metatranscriptómica, analizamos comunidades microbianas en diferentes ecosistemas del suelo, incluyendo agroecosistemas, ambientes naturales y sitios impactados por la actividad humana.
El objetivo es identificar los principales determinantes ecológicos que modelan la estructura y función microbiana.

Los datos generados son analizados mediante pipelines bioinformáticos que permiten la identificación taxonómica y funcional de los microorganismos, la predicción de rutas metabólicas y la detección de genes de resistencia o degradación de compuestos contaminantes.
Esta información es clave para entender cómo las comunidades microbianas responden a las prácticas agrícolas y cómo pueden ser aprovechadas para el diseño de estrategias sostenibles de manejo del suelo.
REGULACIÓN DE LA EXPRESIÓN GÉNICA EN RESPUESTA A CONDICIONES AMBIENTALES ADVERSAS
María Carla Martini, María Florencia Del Papa, Mariano Pistorio
Las bacterias deben responder rápidamente a los cambios ambientales para sobrevivir.
En este proyecto investigamos los sistemas reguladores de expresión génica que se activan frente a estrés por pH, salinidad, temperatura o nutrientes.

Se analizan sistemas de dos componentes y proteínas reguladoras transcripcionales y post-transcripcionales.
Los enfoques genómicos y fisiológicos permiten caracterizar redes regulatorias y entender cómo se coordinan respuestas adaptativas a nivel celular.
Los resultados amplían el conocimiento sobre la plasticidad metabólica bacteriana y su adaptación a condiciones fluctuantes del entorno natural.
Dr. Gonzalo A. Torres Tejerizo
LOS PLÁSMIDOS Y SU ROL EN LA TRANSFERENCIA HORIZONTAL DE GENES
Lucas Castellani, Ileana Salto, Gonzalo Torres Tejerizo, Mariano Pistorio
Los plásmidos son elementos más pequeños que los cromosomas bacterianos y contienen genes que generalmente no se encuentran en el cromosoma. Si bien contribuyen a la diversidad y plasticidad genética de los microorganismos, no son esenciales para la vida microbiana, constituyendo un recurso genético distinto, dinámico y adicional a los genes cromosomales.
Su importancia radica en su papel en la transferencia horizontal de genes y como herramientas para la manipulación genética.
Los plásmidos permiten a las poblaciones bacterianas “muestrear” el pool de elementos genéticos móviles (moviloma), buscando rasgos adaptativos ventajosos ante presiones selectivas locales (resistencia a antibióticos, metales, contaminantes orgánicos o fuentes alternativas de carbono).
En el laboratorio trabajamos en el aislamiento, secuenciamiento y caracterización funcional de recursos genéticos asociados a plásmidos presentes en comunidades bacterianas de ambientes agrícolas y hospitalarios.

Con ello se espera obtener nuevos datos sobre qué tipo de plásmidos se seleccionan (grupo de incompatibilidad/origen de replicación) en cada ambiente y las relaciones entre ellos (interrelación o propagación de información genética).
HERRAMIENTAS MICROBIOLÓGICAS, MOLECULARES Y ÓMICAS APLICADAS AL ESTUDIO DE LA INTERACCIÓN SIMBIÓTICA ENTRE RIZOBIOS Y LEGUMINOSAS
Juliet Nilsson, Gonzalo Torres Tejerizo, Mariano Pistorio
La Fijación Biológica de Nitrógeno (FBN) realizada por bacterias en simbiosis con leguminosas es esencial para la conservación de suelos y la productividad agrícola.
La alfalfa, principal leguminosa forrajera, establece esta simbiosis con rizobios eficientes; sin embargo, su rendimiento se ve afectado en suelos con pH moderadamente bajos.
Se aislaron rizobios denominados Rhizobium favelukesii, tolerantes a la acidez y competitivos para la nodulación de alfalfa, pero ineficientes en FBN.
Estos rizobios son parasíticos y podrían desplazar a Ensifer (Sinorhizobium) meliloti, el rizobio eficiente.
La caracterización de R. favelukesii permitirá comprender mecanismos de tolerancia ácida y de fijación de nitrógeno aún no descritos, posibilitando la creación de variantes más eficientes y tolerantes, con impacto directo en la producción de alfalfa.
BÚSQUEDA DE DETERMINANTES INVOLUCRADOS EN LA DIFERENCIACIÓN DE LOS BACTEROIDES EN LA SIMBIOSIS Medicago–Rhizobium
Gonzalo Torres Tejerizo, Lucas Castellani, Abril Luchetti
La simbiosis Medicago–rhizobia es un proceso complejo que implica la expresión coordinada de numerosos genes tanto en la planta como en la bacteria.
Incluye etapas como la formación de hilos de infección, invasión celular, endocitosis bacteriana y diferenciación de bacteroides, los cuales son responsables de la fijación de nitrógeno.
Mediante análisis transcriptómicos (RNAseq) se buscan identificar genes y mecanismos involucrados en la diferenciación de bacteroides, para comprender mejor el proceso simbiótico y mejorar la productividad de alfalfa.
GENÓMICA FUNCIONAL DE BACTERIAS DE INTERÉS AGRÍCOLA Y BIOTECNOLÓGICO
Mauricio Lozano, Antonio Lagares, Gonzalo Torres Tejerizo
Este proyecto se centra en la secuenciación, ensamblado y anotación funcional de genomas bacterianos aislados de suelos agrícolas de distintas regiones del país.
Buscamos identificar genes asociados con tolerancia al estrés, producción de metabolitos secundarios y mecanismos de interacción planta–microorganismo.
La información genómica obtenida es analizada mediante técnicas de minería de datos y comparación con bases de datos internacionales, lo que permite descubrir nuevos genes de interés biotecnológico y aportar al desarrollo de inoculantes bacterianos de nueva generación.
Este enfoque integrador entre genómica funcional y biología de sistemas proporciona una base sólida para el desarrollo de productos agrícolas más sostenibles y eficientes.

ESTUDIO DE LA INTERACCIÓN BACTERIA–HOSPEDADOR EN SISTEMAS SIMBIÓTICOS Y PATOGÉNICOS
María Carla Martini, Antonio Lagares, Gonzalo Torres Tejerizo
En nuestro grupo abordamos el estudio de las interacciones moleculares y celulares entre bacterias y hospedadores, tanto en relaciones benéficas como patogénicas.
Buscamos entender cómo las bacterias modulan su expresión génica frente a señales del hospedador y cómo estos mecanismos determinan el éxito o fracaso de la colonización.
Utilizamos aproximaciones genómicas, transcriptómicas y proteómicas para identificar determinantes moleculares en la simbiosis o infección.
Estas herramientas permiten analizar globalmente la respuesta bacteriana, identificar reguladores clave y comprender cómo ajustan su metabolismo y fisiología para adaptarse al entorno del hospedador.

Este conocimiento es clave para desarrollar estrategias biotecnológicas que mejoren inoculantes agrícolas o terapias antimicrobianas sostenibles.
Dr. Walter Omar Draghi
ESTUDIOS FUNCIONALES Y ECOLÓGICOS DE MICROORGANISMOS DEL SUELO PARA UNA PRODUCCIÓN AGRÍCOLA SUSTENTABLE
Walter Draghi, Antonio Lagares
La sustentabilidad de los sistemas agrícolas es clave para mantener la productividad de los recursos naturales.
El uso de microorganismos rizosféricos mejora la resistencia de los cultivos frente a condiciones ambientales adversas, promoviendo un crecimiento vegetal saludable.

Se analizan dos ejes principales:
1. Búsqueda de cepas inoculantes más persistentes y eficientes para simbiosis en suelos ácidos.
Se estudian las bases bioquímicas y genéticas de la adaptación a la acidez en Sinorhizobium meliloti, usando técnicas ómicas de expresión global.
Además, se generan fenotipos resistentes (ATR) con mayor capacidad de infección bajo estrés ácido.

2. Estudio de la ecología poblacional de Burkholderia spp. en suelos agrícolas argentinos.
Se analiza su variabilidad genética y funcional en función de las prácticas agrícolas, buscando potenciar su uso como inoculantes biológicos.
APLICACIONES BIOTECNOLÓGICAS DE MICROORGANISMOS EN AGRICULTURA Y AMBIENTE
María Carla Martini, Mauricio Lozano, Walter Draghi
Este eje busca aprovechar el potencial de microorganismos nativos para soluciones biotecnológicas aplicadas a agricultura y biorremediación.
Se estudian cepas capaces de mejorar nutrición vegetal, tolerancia al estrés y degradar contaminantes del suelo.
Se realizan bioensayos en condiciones controladas y en campo para evaluar la eficacia de cepas seleccionadas y su impacto en la productividad.
Además, se estudian los mecanismos moleculares planta–microorganismo para optimizar formulaciones microbianas y su aplicación sustentable.

El objetivo final es generar herramientas biotecnológicas de bajo impacto ambiental que promuevan una agricultura eficiente y sostenible.
Dr. Mauricio J. Lozano
MICROBIOLOGÍA AMBIENTAL Y EVOLUCIÓN DE BACTERIAS DEL SUELO
Mauricio Lozano, Walter Draghi, Antonio Lagares
En el laboratorio investigamos cómo las bacterias del suelo se adaptan a distintos nichos ecológicos y cómo factores como la acidez, la disponibilidad de nutrientes y la presencia de contaminantes moldean su evolución y estructura poblacional.
Nos enfocamos en comunidades rizosféricas y bacterias libres del suelo, integrando herramientas de genómica comparativa, filogenómica y bioinformática avanzada.
A través de estudios de evolución experimental, analizamos la capacidad de cepas nativas para adquirir nuevas funciones adaptativas frente a presiones ambientales, con especial interés en la transferencia horizontal de genes y la dinámica de plásmidos.

Estos estudios contribuyen a comprender los mecanismos de adaptación bacteriana y su potencial aplicación en biotecnología, restauración de suelos degradados y desarrollo de biofertilizantes más eficientes.
ANÁLISIS DE COMUNIDADES MICROBIANAS MEDIANTE SECUENCIACIÓN MASIVA
Mauricio Lozano, Mariano Pistorio, María Florencia Del Papa
Utilizando estrategias de metagenómica y metatranscriptómica, analizamos comunidades microbianas en diferentes ecosistemas del suelo, incluyendo agroecosistemas, ambientes naturales y sitios impactados por la actividad humana.
El objetivo es identificar los principales determinantes ecológicos que modelan la estructura y función microbiana.

Los datos generados son analizados mediante pipelines bioinformáticos que permiten la identificación taxonómica y funcional de los microorganismos, la predicción de rutas metabólicas y la detección de genes de resistencia o degradación de compuestos contaminantes.
Esta información es clave para entender cómo las comunidades microbianas responden a las prácticas agrícolas y cómo pueden ser aprovechadas para el diseño de estrategias sostenibles de manejo del suelo.
GENÓMICA FUNCIONAL DE BACTERIAS DE INTERÉS AGRÍCOLA Y BIOTECNOLÓGICO
Mauricio Lozano, Antonio Lagares, Gonzalo Torres Tejerizo
Este proyecto se centra en la secuenciación, ensamblado y anotación funcional de genomas bacterianos aislados de suelos agrícolas de distintas regiones del país.
Buscamos identificar genes asociados con tolerancia al estrés, producción de metabolitos secundarios y mecanismos de interacción planta–microorganismo.
La información genómica obtenida es analizada mediante técnicas de minería de datos y comparación con bases de datos internacionales, lo que permite descubrir nuevos genes de interés biotecnológico y aportar al desarrollo de inoculantes bacterianos de nueva generación.
Este enfoque integrador entre genómica funcional y biología de sistemas proporciona una base sólida para el desarrollo de productos agrícolas más sostenibles y eficientes.

APLICACIONES BIOTECNOLÓGICAS DE MICROORGANISMOS EN AGRICULTURA Y AMBIENTE
María Carla Martini, Mauricio Lozano, Walter Draghi
Este eje busca aprovechar el potencial de microorganismos nativos para soluciones biotecnológicas aplicadas a agricultura y biorremediación.
Se estudian cepas capaces de mejorar nutrición vegetal, tolerancia al estrés y degradar contaminantes del suelo.
Se realizan bioensayos en condiciones controladas y en campo para evaluar la eficacia de cepas seleccionadas y su impacto en la productividad.
Además, se estudian los mecanismos moleculares planta–microorganismo para optimizar formulaciones microbianas y su aplicación sustentable.

El objetivo final es generar herramientas biotecnológicas de bajo impacto ambiental que promuevan una agricultura eficiente y sostenible.
Dra. María Carla Martini
ESTUDIO DE LA INTERACCIÓN BACTERIA–HOSPEDADOR EN SISTEMAS SIMBIÓTICOS Y PATOGÉNICOS
María Carla Martini, Antonio Lagares, Gonzalo Torres Tejerizo
En nuestro grupo abordamos el estudio de las interacciones moleculares y celulares entre bacterias y hospedadores, tanto en relaciones benéficas como patogénicas.
Buscamos entender cómo las bacterias modulan su expresión génica frente a señales del hospedador y cómo estos mecanismos determinan el éxito o fracaso de la colonización.
Utilizamos aproximaciones genómicas, transcriptómicas y proteómicas para identificar determinantes moleculares en la simbiosis o infección.
Estas herramientas permiten analizar globalmente la respuesta bacteriana, identificar reguladores clave y comprender cómo ajustan su metabolismo y fisiología para adaptarse al entorno del hospedador.

Este conocimiento es clave para desarrollar estrategias biotecnológicas que mejoren inoculantes agrícolas o terapias antimicrobianas sostenibles.
REGULACIÓN DE LA EXPRESIÓN GÉNICA EN RESPUESTA A CONDICIONES AMBIENTALES ADVERSAS
María Carla Martini, María Florencia Del Papa, Mariano Pistorio
Las bacterias deben responder rápidamente a los cambios ambientales para sobrevivir.
En este proyecto investigamos los sistemas reguladores de expresión génica que se activan frente a estrés por pH, salinidad, temperatura o nutrientes.

Se analizan sistemas de dos componentes y proteínas reguladoras transcripcionales y post-transcripcionales.
Los enfoques genómicos y fisiológicos permiten caracterizar redes regulatorias y entender cómo se coordinan respuestas adaptativas a nivel celular.
Los resultados amplían el conocimiento sobre la plasticidad metabólica bacteriana y su adaptación a condiciones fluctuantes del entorno natural.
APLICACIONES BIOTECNOLÓGICAS DE MICROORGANISMOS EN AGRICULTURA Y AMBIENTE
María Carla Martini, Mauricio Lozano, Walter Draghi
Este eje busca aprovechar el potencial de microorganismos nativos para soluciones biotecnológicas aplicadas a agricultura y biorremediación.
Se estudian cepas capaces de mejorar nutrición vegetal, tolerancia al estrés y degradar contaminantes del suelo.
Se realizan bioensayos en condiciones controladas y en campo para evaluar la eficacia de cepas seleccionadas y su impacto en la productividad.
Además, se estudian los mecanismos moleculares planta–microorganismo para optimizar formulaciones microbianas y su aplicación sustentable.

El objetivo final es generar herramientas biotecnológicas de bajo impacto ambiental que promuevan una agricultura eficiente y sostenible.
IDENTIFICACIÓN Y CARACTERIZACIÓN DE COMPUESTOS ANTIMICROBIANOS CON ACTIVIDAD ANTIMICOBACTERIANA
María Carla Martini
La tuberculosis (TB) es la principal causa de muerte por un único agente infeccioso a nivel mundial. La emergencia de resistencia a antibióticos y la diseminación de cepas multirresistentes de Mycobacterium tuberculosis (Mtb), el agente causante de la tuberculosis (TB), limita drásticamente las posibilidades de tratamiento y erradicación. Las infecciones causadas por cepas multirresistentes son difíciles de tratar, requiriendo terapias prolongadas con drogas menos eficaces y con efectos secundarios severos. Además de Mtb, otras micobacterias no tuberculosas (NTM), como M. abscessus (Mab) y M. avium (Mav), están emergiendo como patógenos clínicamente relevantes, particularmente en pacientes inmunocomprometidos, donde las opciones terapéuticas limitadas y las incompatibilidades entre antibióticos complican aún más el tratamiento. Estos escenarios remarcan la necesidad urgente de nuevos antimicrobianos para tratar infecciones causadas por estos patógenos.
En este contexto, en nuestro grupo estamos enfocados en la identificación y caracterización de compuestos antimicrobianos de distinta naturaleza que puedan ser potencialmente utilizados como drogas para tratar infecciones micobacterianas. Nuestro interés esta puesto principalmente en péptidos antimicrobianos (AMPs) y lipopéptidos cíclicos producidos naturalmente por bacterias de distintos géneros y especies.